KI-Tool Für schnelle und kostengünstige Protein-Markierung im Labor
Für die Erforschung von Wechselwirkungen zwischen Molekülen werden Farbstoffe zum Labeln genutzt. Eine kostenlose Software von Nano Temper und Pharm AI verrät, welcher Stoff am besten passt.
Anbieter zum Thema
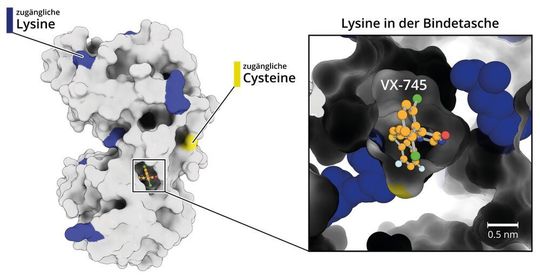
Wechselwirkungen zwischen Proteinen steuern biologische Prozesse im menschlichen Körper. Einblicke in genau diese Vorgänge sind notwendig, um Krankheiten zu verstehen und neue Medikamente entwickeln zu können. Im Labor wird deshalb die Bindungsneigung von Molekülen zu Proteinen gemessen. Für den Nachweis und die Messung dieser Interaktion ist eine Markierung nötig, meist mithilfe eines Farbstoffs. Doch dieser kann die Bindung ungünstig beeinflussen. Wichtig wäre es also zu wissen, welcher Farbstoff die Messung am wenigsten stört. Das Dresdner Start-up Pharm AI und das Münchner Unternehmen Nano Temper Technologies haben dafür nun das gemeinsame Tool „Proto“ entwickelt, welches Zeit und Kosten im Labor sparen soll.
Alpha-Fold-Daten bereits integriert
Die Web-Anwendung „Proto“ soll zusätzliches Vertrauen in die Ergebnisse einer Messung schaffen. „Unsere Web-Applikation schlägt Anwendern den für ihre Messung geeigneten Farbstoff vor“, sagt Christina Wolf, Data Scientist bei Nano Temper. „Das macht Messungen zur Bindungsneigung effizienter und zuverlässiger.“ Um den am besten geeigneten Farbstoff vorherzusagen, nutzt die Software die 3D-Struktur des Proteins. Die Struktur stammt aus der RCSB-Protein-Datenbank oder aus der Strukturdatenbank Alpha Fold des Londoner Unternehmens Deep Mind, einem Tochterunternehmen der Alphabet-Gruppe, zu der auch Google zählt. Erst seit November 2021 hat Deep Mind zusammen mit dem EMBL-EBI die Datenbank frei zugänglich gemacht.
Für die Vorhersage einer Proteinstruktur auf Basis der Aminosäuresequenz des Proteins nutzt Alpha Fold das so genannte Deep Learning – also mehrschichtige künstliche neuronale Netze, die von der Verschaltung der Neuronen im menschlichen Gehirn inspiriert sind. Insgesamt greift Proto damit auf über 700.000 Proteinstrukturen zurück. Nach der Auswahl des Proteins wählen Proto-Nutzer zusätzlich die Bindungsstelle oder das Molekül aus, das ans Zielprotein binden soll. Mit diesen Eingaben vergleicht die Software mögliche Markierungsoptionen, leitet die am wenigsten störende Variante ab und gibt Empfehlungen für die anstehende Messung.

Diese neuartige Labeling-Vorhersage ist der erste wichtige Schritt, um Experimente im Bereich der Biotechnologie und Pharmaindustrie in Zukunft mithilfe künstlicher Intelligenz zu optimieren. „Die Forschenden sparen Zeit, weil aufwändige Untersuchungen zur Validierung der gewählten Markierung entfallen“, beschreibt Pharm-AI-Geschäftsführer Joachim Haupt die Vorteile. Das reduziere Kosten und v. a. auch den Verbrauch von Chemikalien. Die Lösung biete zudem Ansätze für neue Ideen wie die Entwicklung und Integration moderner KI-gestützter Algorithmen für das Screening geeigneter Wirkstoffkandidaten für die Arzneimittelentwicklung.
Kostenfreier Zugang für wichtige Forschung
In den vergangenen Monaten wurde „Proto“ umfangreich getestet, u. a. anhand einer Proteinkinase – einem Enzym, das v. a. in der Krebsforschung eine große Rolle spielt. Die Entwickler möchten, dass Forscher auf diesem und auch auf anderen Gebieten zügiger zu Ergebnissen kommen, indem sie schneller mit Messungen beginnen. Auch aus diesem Grund stellen sie ihr neues Werkzeug kostenlos zur Verfügung. Die Software Proto steht online unter proto.nanotempertech.com zur Verfügung.
(ID:48191266)






:quality(80)/p7i.vogel.de/wcms/c9/16/c9162be8c6014187286dda23e57f8793/0130654555v2.jpeg)
:quality(80)/p7i.vogel.de/wcms/9f/9d/9f9d6fc46606d654deca536f05102f7a/0130752952v1.jpeg)
:quality(80)/p7i.vogel.de/wcms/bb/58/bb58da17d7bb11b44fcae8d06c35df76/0130791510v2.jpeg)
:quality(80)/p7i.vogel.de/wcms/0f/0c/0f0c5774037cc09a3536d24702f6204b/0130936383v2.jpeg)
:quality(80)/p7i.vogel.de/wcms/dc/7b/dc7b0f7209d2dedf548b5019da2e1b9c/0130556742v1.jpeg)
:quality(80)/p7i.vogel.de/wcms/bf/30/bf3038b92e4988d6c883c155ef727153/0130924147v3.jpeg)
:quality(80)/p7i.vogel.de/wcms/a6/e0/a6e0ab14cf7f6b22d536f6ca6e5fb777/0130793394v2.jpeg)
:quality(80)/p7i.vogel.de/wcms/63/85/638523e67603079a004bbd3a99b6ad92/0130856502v1.jpeg)
:quality(80)/p7i.vogel.de/wcms/df/3d/df3d3f7d7b425eabae87bab4ef68bd6c/0130259765v1.jpeg)
:quality(80)/p7i.vogel.de/wcms/b9/32/b9326aa0b6f26d5e5eeee82c86aab8b6/0130976290v2.jpeg)
:quality(80)/p7i.vogel.de/wcms/2d/5f/2d5f14d92ec22f38682c6d240600579f/0131000090v1.jpeg)
:quality(80)/p7i.vogel.de/wcms/19/40/194054b15f3c0e161583d7ea8917ec3f/0130974372v2.jpeg)
:quality(80)/p7i.vogel.de/wcms/e2/5e/e25e2c9f40617e17d32524787c6ece1d/0130248690v1.jpeg)
:quality(80)/p7i.vogel.de/wcms/09/88/09883aaf7db3151a2e894d56c2a515d4/0130982666v2.jpeg)
:fill(fff,0)/images.vogel.de/vogelonline/companyimg/6400/6447/65.jpg)
:fill(fff,0)/p7i.vogel.de/companies/68/07/6807ad98568ce/logo-elementar-rgb.jpeg)
:fill(fff,0)/p7i.vogel.de/companies/63/9c/639c7cce17c0a/pce-instruments-logo-300dpi.png)
:quality(80)/p7i.vogel.de/wcms/bc/b1/bcb1a281554b42beb4bdf6a90a06e409/0124275766v2.jpeg)
:quality(80)/p7i.vogel.de/wcms/87/eb/87eb8197e51c5617896dabeb9f5c8a31/0126638370v4.jpeg)