Antibiotikaresistenzen Jede Minute zählt: Antibiotikaresistenzen mit Software vorhersagen
Jedes Jahr sterben in der Europäischen Union etwa 25.000 Menschen an antibiotikaresistenten und damit schwer behandelbaren Bakterien. Bisherige Laborverfahren zur Bestimmung solcher Antibiotikaresistenzen sind zeitaufwändig. Mithilfe einer umfassende Gendatenbank und leistungsfähige Algorithmen wollen Partner aus Industrie und Forschung solche Resistenzen vorhersagen. Bioinformatiker der Universität des Saarlandes waren an der computergestützten Analyse der Gendaten beteiligt.
Anbieter zum Thema
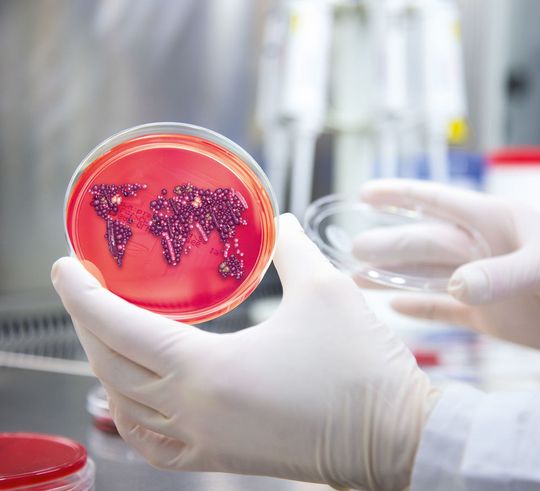
Saarbrücken – Vor wenigen Tagen hat die Weltgesundheitsorganisation WHO eine Liste von zwölf Bakterienstämmen veröffentlicht, die aufgrund ihrer Resistenz „die größte Bedrohung“ für die globale Gesundheit darstellen, so die WHO. An diesen Resistenzen forscht auch Andreas Keller, Professor für Klinische Bioinformatik an der Universität des Saarlandes. „Wenn Patienten rasch Zugang zu der Therapie erhalten, die am besten geeignet ist, den Krankheitserreger zu bekämpfen, ist es nicht nur zum Vorteil des Patienten. Es kann auch dazu beitragen, die momentan vorhandenen Antibiotika gezielter einzusetzen, um die Entstehung von Resistenzen zu verlangsamen“, erklärt er seinen Ansatz.
Bisherige Verfahren sind zeitaufwändig
Bisherige Verfahren, um solche Resistenzen zu entlarven, sind zeitaufwändig. Die Bakterien werden auf Nährböden in einer Petrischale gezüchtet, bis sie sichtbar sind und ihr Ansprechverhalten auf Antibiotika getestet werden kann. Bis zum endgültigen Ergebnis vergeht so für den Kranken kostbare Zeit. „Erst nach 24 bis 72 Stunden weiß der Arzt sicher, mit welchem Antibiotikum er behandeln muss. Kein Mediziner lässt einen Patienten so lange leiden, also verlässt er sich auf seine Erfahrung“, erklärt Achim Plum, Chief Commercial Officer von Curetis. „Wenn er das falsche Antibiotikum einsetzt, ist dem Patienten nicht geholfen. Aber nicht nur das: mit jeder Gabe von Antibiotika besteht das Risiko, dass resistente Erreger entstehen. Da sich Bakterien sehr schnell vermehren, ist das Evolution im Zeitraffer“, so Plum.
Schon jetzt vertreibt das Unternehmen aus Baden-Württemberg Schnelltests, die mithilfe von speziellen Molekülen Erreger und deren Resistenzen bei Lungenentzündungen, Gewebs- und Implantatsinfektionen sowie Infektionen von Blut und Bauchhöhle erkennen. „Im Moment verwenden wir die genetischen Antibiotika-Resistenz-Marker, die man bereits seit längerem kennt. Damit decken wir die derzeit am weitesten verbreiteten Resistenzmechanismen ab. Wir wissen aber, dass uns damit Resistenzen entgehen”, sagt Achim Plum. „Wir wollen daher auch die derzeit noch weniger häufigen Resistenzmechanismen entschlüsseln, weil sie in Zukunft womöglich eine große Bedrohung darstellen.“ Um entsprechende Tests zu entwickeln, braucht es Untersuchungen an hunderten oder tausenden von Erregern, die aus Patienten isoliert wurden. „Wir benötigen dabei sowohl die vollständige genetische Information der Pathogene als auch ihr Ansprechverhalten gegenüber gängigen Antibiotika, damit wir einen Zusammenhang zwischen Resistenz und der zugrundeliegenden genetischen Veränderung herstellen können“, erläutert Plum.
Datenbank mit 11.000 Bakterienstämme und Reaktionsmuster zu 21 Antibiotika
Um das zu erreichen, erwarb Curetis im September des vergangenen Jahres von der Siemens Technology Accelerator GmbH die Gendatenbank GEAR, was für „Genetic Antibiotic Resistance and Susceptibility“ steht. Die Datenbank und dazugehörige Plattform wurde in Zusammenarbeit mit zwei Universitäten entwickelt. Das Institut für Klinische Molekularbiologie in Kiel war für die Gensequenzierung der Bakterien zuständig, Professor Andreas Keller und seine Arbeitsgruppe „Klinische Bioinformatik“ an der Universität des Saarlandes übernahmen die computergestützte Analyse des 30-Terabyte-Datenbestandes.
„Bakterien sind unheimlich clever und setzen ihre Genanlagen für Resistenzen sehr schnell um. Mithilfe von GEAR können wir nun ihre Strategien nachvollziehen“, sagt Bioinformatiker Keller. Voraussetzung dafür ist eine weltweite Datenbasis, die über Jahrzehnte reicht. Deswegen enthält GEAR 11.000 Bakterienstämme und Reaktionsmuster zu 21 Antibiotika, die in den vergangenen drei Jahrzehnten aus Patientenproben rund um den Globus isoliert wurden.
Mithilfe der Daten prüfen die Forscher, welche genetischen Auffälligkeiten mit der jeweiligen Antibiotika-Resistenz zusammenhängen. „Das ist ein gigantisches Puzzle“, sagt Keller und rechnet aus, dass die untersuchte Datenmenge knapp 500.000 Bibeln entspricht. Seine Algorithmen und erste Ergebnisse geben ihm Zuversicht: „Wir können die Resistenzen bereits zu 85 Prozent vorhersagen“, so Keller.
Resistenzen gegen alte und neue Antibiotika entwickeln sich dynamisch weiter. Daher soll sich auch die GEAR-Datenbank weiter entwickeln. „Antibiotikaresistenz ist eines der drängendsten Probleme der Gesundheitsversorgung weltweit und muss koordiniert angegangen werden. Wir beabsichtigen GEAR im Schulterschluss zwischen akademischer Forschung, öffentlichem Gesundheitswesen und Industrie zu einer gemeinsamen Forschungsplattform für Antibiotikaresistenzen auszubauen“, sagt Plum.
Das Projekt wird auf der Computermesse Cebit vom 20. bis 24. März in Hannover in Halle 6 am Stand E28 vorgestellt.
(ID:44569730)






:quality(80)/p7i.vogel.de/wcms/48/0e/480e6d0c7a7a9afe60023e5560c00b30/0131243004v2.jpeg)
:quality(80)/p7i.vogel.de/wcms/96/f4/96f41136c248248817210b7df8296c6e/0131243044v2.jpeg)
:quality(80)/p7i.vogel.de/wcms/fb/49/fb49fffcc5b2584659c1a81932ab3c55/0131215424v1.jpeg)
:quality(80)/p7i.vogel.de/wcms/d8/94/d8946bebf210c5826a6bfd51d610eedc/0130122950v2.jpeg)
:quality(80)/p7i.vogel.de/wcms/a8/9a/a89a4fd1c2742eb96d85ff270e9f52d4/0131047740v1.jpeg)
:quality(80)/p7i.vogel.de/wcms/dc/7b/dc7b0f7209d2dedf548b5019da2e1b9c/0130556742v1.jpeg)
:quality(80)/p7i.vogel.de/wcms/bf/30/bf3038b92e4988d6c883c155ef727153/0131240119v5.jpeg)
:quality(80)/p7i.vogel.de/wcms/ce/d1/ced1a66ddc5248ac5c86aa873b3c8d5a/0131387387v2.jpeg)
:quality(80)/p7i.vogel.de/wcms/ba/32/ba322cc757f2f82da2839729e0648ca0/0131377715v2.jpeg)
:quality(80)/p7i.vogel.de/wcms/7a/3e/7a3e9478433a525b34c6b34a0aab133f/0131322665v1.jpeg)
:quality(80)/p7i.vogel.de/wcms/39/f1/39f132a693501496c01f691584eafa75/0131244447v2.jpeg)
:quality(80)/p7i.vogel.de/wcms/04/49/044958b43723ceca42410feb766079ae/0131240585v2.jpeg)
:quality(80)/p7i.vogel.de/wcms/bb/e9/bbe97af9120730250441d33706d76f2a/0131122618v1.jpeg)
:quality(80)/p7i.vogel.de/wcms/3c/0f/3c0f1dc6670ceea51950c2b0fc339173/0131057362v2.jpeg)
:quality(80)/p7i.vogel.de/wcms/23/06/230661a2a04bee677a45d46844a77317/0131368963v2.jpeg)
:fill(fff,0)/images.vogel.de/vogelonline/companyimg/27600/27667/65.jpg)
:fill(fff,0)/images.vogel.de/vogelonline/companyimg/86900/86921/65.jpg)
:fill(fff,0)/p7i.vogel.de/companies/69/a7/69a7ea89887e5/thg-logo-oclaim-rgb.png)
:quality(80)/p7i.vogel.de/wcms/18/d9/18d9283f0c3e897e0e0a3c155496bebc/0125083957v2.jpeg)
:quality(80)/p7i.vogel.de/wcms/ba/26/ba26196be97de79257deda740400464a/0130614035v2.jpeg)