Big Data im Darm Neue Ansätze zur Analyse biomedizinischer Mikrobiomdaten
Das Mikrobiom von gesunden und erkrankten Menschen ist ein Datenpool mit hohem Potenzial. Dabei geht es vor allem auch um das tiefe Verständnis der Interaktionen einer Vielzahl von Bakterienarten untereinander und mit den Darmzellen. Hier sind neue Ansätze der Datenanalyse gefragt.
Anbieter zum Thema
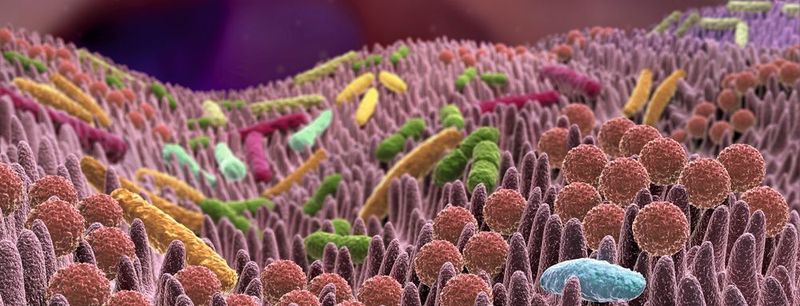
In den letzten Jahren ist durch eine Vielzahl empirischer Studien deutlich geworden, dass das Ensemble von Mikroorganismen im menschlichen Darm, ihre Wechselwirkungen untereinander und mit den Darmzellen, also das Mikrobiom, von großer klinischer Bedeutung sind.
Es sind (mit heutigen Methoden) etwa N = 500 verschiedene Taxa (auf der phylogenetischen Ebene der Gattung) in einem typischen Mikrobiom nachweisbar. Eine der aktuell wichtigsten öffentlichen Datenbanken zu Mikrobiomzusammensetzungen, das US-amerikanische Human Microbiome Project, enthält zum Beispiel über 2200 Mikrobiome aus Stuhlproben [1]. Zur Zeit werden zudem Mikrobiomzusammensetzungen aus einer Vielzahl klinischer Studien verfügbar, sodass die Rolle des Mikrobioms im klinischen Kontext immer fundierter untersucht werden kann.
Kombinatorisch bestehen damit N(N–1)/2 Interaktionsmöglichkeiten („jeder mit jedem“), die vorliegen oder fehlen und, falls sie vorliegen, zudem positiv (synergetisch) oder negativ (kompetitiv) sein können. Damit sind 3 hoch N(N-1)/2 verschiedene Netzwerke möglich, das wären bereits mehr Möglichkeiten als im Weltall Atome vermutet werden.
Auf einer etwas mikroskopischeren Ebene, nämlich im Metabolismus dieser Mikroorganismen, lassen sich die Interaktionen auf den Austausch von und den Wettbewerb um chemische Stoffe herunterbrechen. Diese Spezies spannen so ein riesiges Netzwerk vieler tausend biochemischer Reaktionen auf. Über Sekretion und Aufnahme chemischer Substanzen sind die Spezies untereinander und mit den sie umgebenden Darmzellen verzahnt. Eine kürzliche Studie [2] schätzt auf der Grundlage der aktuellen (immer noch unvollständigen) Kenntnis metabolischer Reaktionen etwa 2300 solche metabolische Wechselwirkungen als Fundament der beschriebenen mikrobiellen Interaktionsnetzwerke und etwa 700 metabolische Wechselwirkungen der Mikroorganismen mit den menschlichen Darmzellen.
Das Mikrobiom ist also ein komplexes, mit dem Darm verzahntes System, das von hoher Bedeutung für die Gesundheit ist. Und durch die Kombinatorik der Interaktionen, durch die aktuell explodierende Datengrundlage von Mikrobiomzusammensetzungen und durch sein metabolisches Fundament ist das Mikrobiom zudem ein Beispiel für „Big Data“ in der Biologie.
Automatische statistische Mikrobiomanalyse
Moderne Sequenziertechnik hat in der Biologie längst das Zählen und Zeichnen ersetzt – anstelle des Mikroskopierbildes treten 16S rRNA-Sequenzierdaten die mit Standardmethoden in Taxa klassifiziert werden.
Mit den so gewonnenen Häufigkeitstabellen erhält man ein Datenformat, bei dem jede einzelne Probe zu einem Abundanz- oder Häufigkeitsvektor führt. In biomedizinischen Datenbanken werden nun sehr viele dieser Dateneinträge gesammelt und können, bei medizinischen Daten systematisch anonymisiert, nach Phänotypen und weiteren Annotationen selektiert und extrahiert werden. Für jeden dieser Datensätze ergibt sich damit die Möglichkeit, die Auftretensmuster der Mikroorganismen systematisch zu studieren und zu analysieren.
Daraus ergeben sich allerdings einige statistische Fallstricke, denn die feine Auflösung der über 500 Gattungen ergibt bereits 499 x 500 / 2 Paare von Gattungen, deren gemeinsames Auftreten oder deren Verdrängung zu untersuchen wären. Es ist offensichtlich, dass hier eine enorme Zahl von Proben zu vergleichbaren Versuchsbedingungen genommen werden müsste, um über eine klassische Korrelationsanalyse zu signifikanten Ergebnissen zu gelangen. Zudem sind die Mikroorganismen in ihrer Häufigkeit sehr unterschiedlich und gerade die seltener vorkommenden Organismen („the rare biosphere“ [2]) sind medizinisch oft von besonderem Interesse.
(ID:44899305)







:quality(80)/p7i.vogel.de/wcms/07/29/072962cf54ce048cab6f90214fc58418/image1v1.jpeg)
:quality(80)/p7i.vogel.de/wcms/4a/b6/4ab66927b81ebf966a41081699111fdc/0131598871v2.jpeg)
:quality(80)/p7i.vogel.de/wcms/6c/93/6c93b004f1e78deb7e24da3318766f84/0131138303v2.jpeg)
:quality(80)/p7i.vogel.de/wcms/63/2b/632b7c3001c517c32711dac6298f8707/0131501813v2.jpeg)
:quality(80)/p7i.vogel.de/wcms/26/d4/26d4f76786d5636186b53e0460f122ad/0131515490v2.jpeg)
:quality(80)/p7i.vogel.de/wcms/43/b5/43b5b01a01e23c21009d2ca43e73bc5e/0131461156v2.jpeg)
:quality(80)/p7i.vogel.de/wcms/fb/49/fb49fffcc5b2584659c1a81932ab3c55/0131215424v1.jpeg)
:quality(80)/p7i.vogel.de/wcms/a8/9a/a89a4fd1c2742eb96d85ff270e9f52d4/0131047740v1.jpeg)
:quality(80)/p7i.vogel.de/wcms/7b/c9/7bc945fec5ec26d7c154890235f42e31/0131662861v1.jpeg)
:quality(80)/p7i.vogel.de/wcms/1b/a2/1ba2d027a8c41332bd5ac2f897250113/0131662713v1.jpeg)
:quality(80)/p7i.vogel.de/wcms/c7/92/c792a20f82cca86e2414ee97590b3b29/0131648572v2.jpeg)
:quality(80)/p7i.vogel.de/wcms/30/1f/301f895fd254453cc7b2126baa944002/0131635672v1.jpeg)
:quality(80)/p7i.vogel.de/wcms/31/9f/319fb620749d359ee20c28483338dc0e/0131664573v1.jpeg)
:quality(80)/p7i.vogel.de/wcms/a0/4d/a04d0563072b334bd4cdc0b5ce498763/0131540240v1.jpeg)
:quality(80)/p7i.vogel.de/wcms/d1/d5/d1d5f369ad43bff37d037f8319c35488/img-5661-jpg-2016x1134v1.webp)
:quality(80)/p7i.vogel.de/wcms/04/49/044958b43723ceca42410feb766079ae/0131240585v2.jpeg)
:fill(fff,0)/images.vogel.de/vogelonline/companyimg/20500/20552/65.jpg)
:fill(fff,0)/images.vogel.de/vogelonline/companyimg/6400/6447/65.jpg)
:fill(fff,0)/p7i.vogel.de/companies/5e/32/5e32fc50e1029/socorex.jpg)
:quality(80)/images.vogel.de/vogelonline/bdb/1307100/1307125/original.jpg)
:quality(80)/images.vogel.de/vogelonline/bdb/1307100/1307126/original.jpg)
:quality(80)/p7i.vogel.de/wcms/7b/c9/7bc945fec5ec26d7c154890235f42e31/0131662861v1.jpeg)
:quality(80)/p7i.vogel.de/wcms/ae/14/ae14c0efb9ba19c5d7334b2a6edca296/0127379090v2.jpeg)