SEC-MALS Detektivarbeit am Detektor
Die Mehrwinkel-Lichtstreuungs-Messung (MALS) hat seit Beginn ihres Einsatzes in der makromolekularen Analytik wesentlich dazu beigetragen, fundamentale Fortschritte im Verständnis vieler biophysikalischer Vorgänge zu erzielen. Davon profitiert beispielsweise auch die biomedizinische Forschung.
Anbieter zum Thema
Lichtstreudetektoren, speziell für die Mehrwinkel-Lichtstreuungs-Messung (MALS), sind inzwischen zu einem weithin eingesetzten, kaum mehr wegzudenkenden Werkzeug für die biophysikalische Charakterisierung von Biomolekülen verschiedenster Art geworden. Oftmals werden sie an Trennsysteme wie etwa die Feldfluss-Fraktionierung (AF4) oder auch die klassische SEC (Größen-Ausschluss-Chromatographie) gekoppelt. So liefert diese Technologie die Molekülgewichte der einzelnen Komponenten in der Probe, und diese Bestimmung ist absolut, d.h. sie benötigt keinerlei Standards zum Abgleich oder Annahmen über die zu messenden Moleküle. Zudem liefert MALS (oder auch Statische Lichtstreuung, SLS) den Gyrations-Radius (Rg) der Bestandteile sowie zusätzliche Informationen über die Zusammensetzung (Poly- oder Monodispersität) einer Probe aus Biomolekülen. Nutzt man zudem noch online die Dynamische Lichtstreuung (DLS), erhält man zusätzlich noch den hydrodynamischen Radius (Rh) der Moleküle. Mittels SEC-MALS misst man das absolute Molekulargewicht von Makromolekülen, und zwar unabhängig von deren Elutionsvolumen aus der Säulentrennung. Daher eignet sich MALS auch besonders gut zur Messung von Proben, die aufgrund von Wechselwirkungen mit dem Säulenmaterial ein atypisches Elutionsverhalten zeigen. Die Messmethode kann zudem im Batch-Modus unspezifische Interaktionen zwischen Proteinen nachweisen.
SEC-MALS bietet eine Fülle von Anwendungen. So lässt sich etwa das Molekülgewicht von gelösten Makromolekülen bestimmen oder eine Lösung auf das Vorhandensein von Aggregaten überprüfen. Die Stöchiometrie von Proteinkomplexen in Lösung kann man ebenso aufklären wie den Grad der Konjugierung von Polypeptiden, ganz gleich, ob es sich dabei um eine Glykosylierung, PEGylierung oder auch um einen Komplex mit Lipiden und Detergentien handelt.
Im Labor für Molekularbiologie am Medical Research Council (MRC) im britischen Cambridge versuchen die Wissenschaftler, Fortschritte im Verständnis biologischer Vorgänge auf molekularbiologischem Niveau zu erreichen. Die dabei erzielten Erkenntnisse sollen letztlich zur Aufklärung fundamentaler Prozesse bei menschlichen Erkrankungen beitragen. Von strukturellen Untersuchungen an isolierten Makromolekülen versucht man über deren Zusammenwirken Schlüsse daraus zu ziehen, wie subzelluläre Vorgänge ablaufen, um dann weiter zu einer Gesamtsicht auf Zellen, Organe und letztlich vollständige Organismen zu gelangen. Das Forschungsinstitut wählte Instrumente für die Lichtstreuung aus, um seine Abteilung für Biophysik mit den leistungsfähigsten Werkzeugen auszustatten.
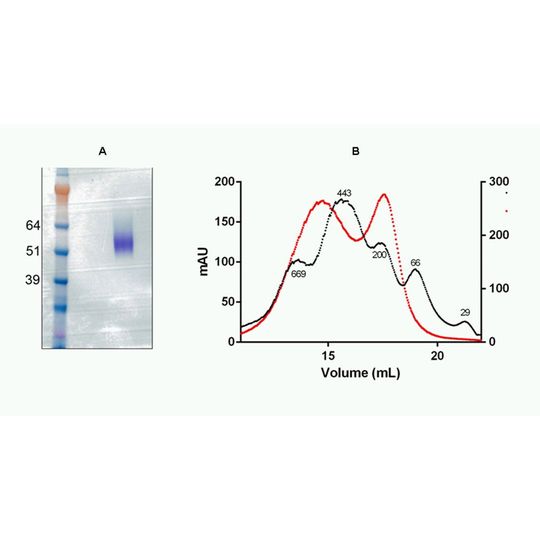
Ein rekombinantes Protein wurde exprimiert und aufgereinigt. Dann folgte die Bestimmung seines Molekülgewichtes in Lösung. Hierzu diente zunächst die analytische SEC, wobei sich Werte zwischen 200 und 700 kDa ergaben (s. Abb. 1).
Analytische Detektivarbeit
Dieses Resultat überraschte, lag doch das berechnete Molekulargewicht, das aus der Abfolge der Aminosäuren abgeleitet wurde, lediglich bei 46 kDa. Hinzu kam der Befund, wonach das Protein bei der Trennung mittels konventioneller Säulen in Form von zwei Peaks erscheint (s. Abb. 1B, rot). Und schließlich waren diese beiden Peaks auch noch eindeutig größer als es im Vergleich mit den Protein-Standards (s. Abb. 1 B, schwarz) zu erwarten gewesen wäre. Wie kam aber nun diese Diskrepanz zustande? Aufschluss darüber lieferte die Gel-Elektrophorese unter nicht-reduzierenden, sog. nativen Bedingungen. Bei dieser Trenntechnik bleiben die innermolekularen Disulfidbrücken erhalten, die dem Protein seine native Tertiärstruktur geben und die monomere Molekülform begünstigen. Unter diesen Umständen wanderten die Proteinmoleküle nun tatsächlich etwa so weit, wie es entsprechend ihrem theoretisch abgeleiteten Molekülgewicht für das Monomer zu erwarten war (s. Abb. 1A). Eine mögliche Aggregatbildung durch Bildung von Disulfidbrücken zwischen verschiedenen Proteinmolekülen wurde so verhindert und die Moleküle lagen weitgehend als Monomere vor. Dieses Beispiel verdeutlicht, dass die Wahl der experimentellen Bedingungen einen enormen Einfluss auf das Resultat ausübt und dieses unter Umständen stark verändern kann.
(ID:43453409)







:quality(80)/p7i.vogel.de/wcms/63/2b/632b7c3001c517c32711dac6298f8707/0131501813v2.jpeg)
:quality(80)/p7i.vogel.de/wcms/48/0e/480e6d0c7a7a9afe60023e5560c00b30/0131243004v2.jpeg)
:quality(80)/p7i.vogel.de/wcms/96/f4/96f41136c248248817210b7df8296c6e/0131243044v2.jpeg)
:quality(80)/p7i.vogel.de/wcms/fb/49/fb49fffcc5b2584659c1a81932ab3c55/0131215424v1.jpeg)
:quality(80)/p7i.vogel.de/wcms/26/d4/26d4f76786d5636186b53e0460f122ad/0131515490v2.jpeg)
:quality(80)/p7i.vogel.de/wcms/43/b5/43b5b01a01e23c21009d2ca43e73bc5e/0131461156v2.jpeg)
:quality(80)/p7i.vogel.de/wcms/a8/9a/a89a4fd1c2742eb96d85ff270e9f52d4/0131047740v1.jpeg)
:quality(80)/p7i.vogel.de/wcms/39/fe/39fe2cd50f7947927c078ad83987abf2/microbiome-04-jpg-2cqtransformid-3d15081-2casite-3ddefaultde-pagespeed-ce--ofz-tqfod-750x422v1.jpeg)
:quality(80)/p7i.vogel.de/wcms/cd/e5/cde57faefc6531041e587a2fde0220ef/image1-1322x744v1.jpeg)
:quality(80)/p7i.vogel.de/wcms/13/8f/138f41de403c0c81139657dae230188d/0131503024v1.jpeg)
:quality(80)/p7i.vogel.de/wcms/25/1f/251fac2058dce921eba03b6e830876ec/0131426881v2.jpeg)
:quality(80)/p7i.vogel.de/wcms/a0/4d/a04d0563072b334bd4cdc0b5ce498763/0131540240v1.jpeg)
:quality(80)/p7i.vogel.de/wcms/d1/d5/d1d5f369ad43bff37d037f8319c35488/img-5661-jpg-2016x1134v1.webp)
:quality(80)/p7i.vogel.de/wcms/04/49/044958b43723ceca42410feb766079ae/0131240585v2.jpeg)
:quality(80)/p7i.vogel.de/wcms/57/11/5711ba14776b6e702c9e775a14837239/0131582930v2.jpeg)
:fill(fff,0)/images.vogel.de/vogelonline/companyimg/20500/20552/65.jpg)
:fill(fff,0)/p7i.vogel.de/companies/68/07/6807ad98568ce/logo-elementar-rgb.jpeg)
:fill(fff,0)/images.vogel.de/vogelonline/companyimg/69800/69835/65.jpg)
:quality(80)/images.vogel.de/vogelonline/bdb/909100/909152/original.jpg)
:quality(80)/images.vogel.de/vogelonline/bdb/909100/909153/original.jpg)
:quality(80)/images.vogel.de/vogelonline/bdb/909100/909154/original.jpg)
:quality(80)/images.vogel.de/vogelonline/bdb/909100/909155/original.jpg)
:quality(80)/p7i.vogel.de/wcms/68/02/680272d28efb89d85e65d8bb07de7e93/0130542168v2.jpeg)
:quality(80)/p7i.vogel.de/wcms/68/04/68042597b0987dc4d57c3b541f8e3b16/0128181173v2.jpeg)